Wirtualne laboratorium (WL‑I)
Przeprowadź doświadczenie w pracowni genetycznej. Rozwiąż problem badawczy, zapisz wyniki, sformułuj wnioski i zweryfikuj hipotezę.
Prawidłowa sekwencja początkowego fragmentu genu łańcucha beta hemoglobiny:
GTG CAT CTG ACT CCT GAG GAG
Temat: Sekwencjonowanie genu łańcucha beta hemoglobiny metodą Sangera
Problem badawczy: Czy sekwencja genu łańcucha beta hemoglobiny w pobranej próbce DNA jest prawidłowa?
Hipoteza 1: Sekwencja genu łańcucha beta hemoglobiny w badanej próbce jest prawidłowa.
Hipoteza 2: Sekwencja genu łańcucha beta hemoglobiny w badanej próbce nie jest prawidłowa.
Sprzęt laboratoryjny:
4 puste probówki Eppendorfa na statywie
pipeta automatyczna o objętości 10–100 mul
żel agarozowy
Odczynniki:
próbka z matrycowym DNA
mieszanina dideoksynukleotydów
ddATP znakowany żółtym barwnikiem
ddCTP znakowany niebieskim barwnikiem
ddGTP znakowany czerwonym barwnikiem
ddTTP znakowany zielonym barwnikiem
polimeraza DNA
Zasób interaktywny dostępny pod adresem https://zpe.gov.pl/a/DW7wIQZDs
Laboratorium 1
Przeprowadzono doświadczenie w pracowni genetycznej.
Prawidłowa sekwencja początkowego fragmentu genu łańcucha beta hemoglobiny: GTG CAT CTG ACT CCT GAG GAG.
Temat: Sekwencjonowanie genu łańcucha beta hemoglobiny metodą Sangera
Problem badawczy: Czy sekwencja genu łańcucha beta hemoglobiny w pobranej próbce DNA jest prawidłowa?
Hipoteza 1: Sekwencja genu łańcucha beta hemoglobiny w badanej próbce jest prawidłowa.
Hipoteza 2: Sekwencja genu łańcucha beta hemoglobiny w badanej próbce nie jest prawidłowa.
Sprzęt laboratoryjny: cztery puste probówki Eppendorfa na statywie; pipeta automatyczna o objętości od 10 do 100 mul; żel agarozowy.
Odczynniki: próbka z matrycowym DNA; mieszanina dideoksynukleotydów; ddATP znakowany żółtym barwnikiem; ddCTP znakowany niebieskim barwnikiem; ddGTP znakowany czerwonym barwnikiem; ddTTP znakowany zielonym barwnikiem; polimeraza DNA.
Instrukcja:
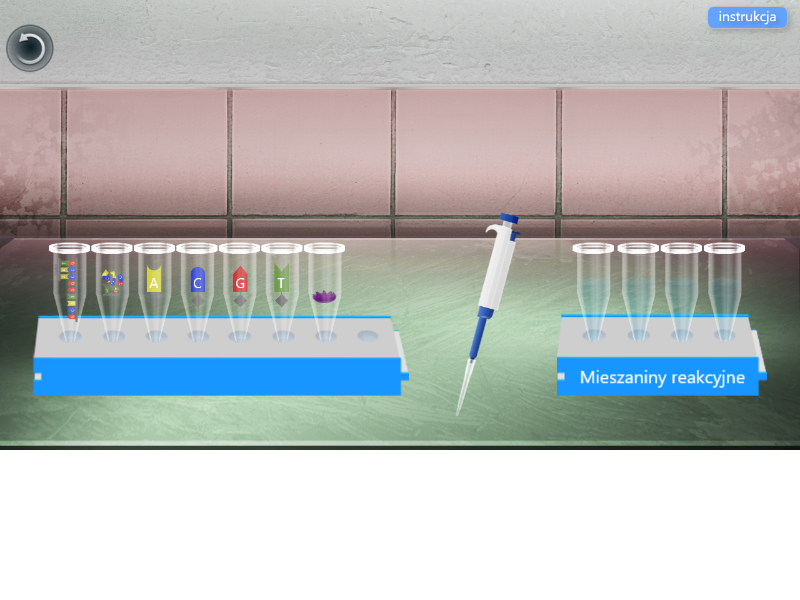
1. Przygotowano mieszaninę reakcyjną do reakcji łańcuchowej polimerazy PCR. Do czterech probówek Eppendorfa dodano za pomocą pipety automatycznej:
- 5 mikrolitrów matrycy DNA - z radioaktywnie wyznakowanym starterem;
- 10 mikrolitrów mieszaniny deoksynukleotydów;
- 3 mikrolitry dideoksynukleotydów (do każdej z probówek Eppendorfa inny rodzaj: ddATP, ddCTP, ddGTP, DDTTP).
2. Włożono cztery probówki Eppendorfa zawierające mieszaniny reakcyjne do termocyklera i przeprowadzono PCR.
3. Po zakończeniu PCR pobrano pipetą automatyczną po 10 mikrolitrów próbek Eppendorfa. Umieszczono je w studzienkach w żelu agarozowym. Przeprowadzono elektroforezę DNA.
4. Odczytano sekwencję DNA bezpośrednio z żelu. Wykonano ćwiczenia interaktywne.
Szczegóły zjawiska 1
Przyłączenie dideoksynukleotydu uniemożliwia dalsze wydłużanie nici DNA przez polimerazę, ponieważ jest on pozbawiony grupy –OH w pozycji 3′, więc nie ma możliwości utworzenia wiązania fosfodiestrowego z kolejnym nukleotydem.
Szczegóły zjawiska 2
Do sekwencjonowania stosuje się wysoko rozdzielczą elektroforezę żelową, która umożliwia rozróżnienie nawet tych łańcuchów DNA, które różnią się tylko jednym nukleotydem.
Szczegóły zjawiska 3
Stężenie deoksynukleotydu musi być znacznie wyższe niż stężenie odpowiedniego dideoksynukleotydu, aby umożliwić wytworzenie wystarczającej liczby fragmentów przy jednoczesnej transkrypcji całej sekwencji.
Wyniki: DNA pochodzący z badanej próbki ma sekwencję: GTG CAT CTG ACT CCT GTG GAG.
Wnioski: Fragment DNA zawiera mutację punktową w szóstym kodonie genu podjednostki beta hemoglobiny.
Weryfikacja hipotezy: Hipoteza 1 jest fałszywa. Hipoteza 2 jest prawdziwa.